首页 > Python资料 博客日记
基于LIDC-IDRI肺结节肺癌数据集的放射组学机器学习分类良性和恶性肺癌(Python 全代码)全流程解析 (一)
2024-06-05 22:00:05Python资料围观345次
基于LIDC-IDRI肺结节肺癌数据集的放射组学深度学习分类良性和恶性肺癌(Python 全代码)全流程解析 (一)
第二部分传送门
第三部分传送门
1 LIDC-IDRI数据集介绍
LIDC-IDRI数据集是用于医学影像分析的公开数据集,包含1010例低剂量CT扫描和人工标注的肺部结节信息。这些数据对于肺癌早期检测和算法开发至关重要。由美国国立卫生研究院(NIH)资助,该数据集为研究人员提供了宝贵资源,促进了医学影像处理和人工智能在肺部疾病诊断方面的进展,。
数据集下载地址如下:*https://www.cancerimagingarchive.net/collection/lidc-idri/*该数据集大小为133GB,数据集的下载需要下载器和稳定的网络,否则可能失败。
下载方面存在问题的私信我,我有完成数据集
1.1数据集预处理
数据集的预处理一共分为三个部分,图像的归一化,肺结节感兴趣区域分割,良恶性肺结节标注提取。
LIDC-IDRI数据结构如下:

1.1.1 图像读取-(python库pylidc安装)
在预处理图像过程中,我们不需要自己写程序去解析所有的文件。已经有人早就写好了免费的库文件去解析数据集。即为python的pylidc库。该库的安装如下:
打开anaconda prompt 输入
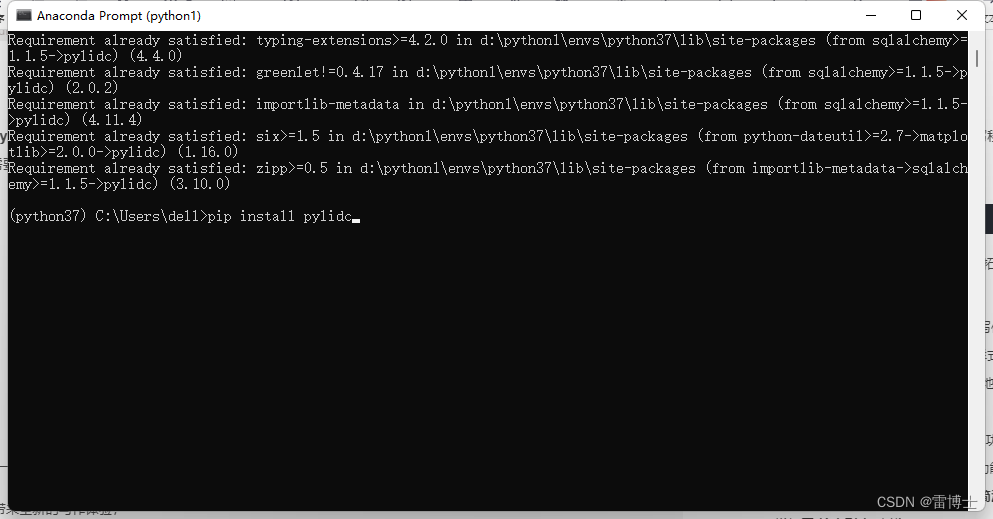
pip install pylidc
注意在安装完该库后,需要在系统用户文件夹下,新建pylidc.conf文件,为该库的运行指明文件存放的位置。
[dicom]
path = G:\dataset_zhang\LIDC-IDRI
将以上路径修改为数据集存放的路径。
测试该库是否安装成功代码如下:
import pylidc as pl
from pylidc.utils import consensus
import os
dataset_path = r'G:\dataset_zhang\LIDC-IDRI\\'#修改路径哦
dicom_name = 'LIDC-IDRI-0001'
PathDicom = os.path.join(example) # 构建当前病例文件夹的完整路径
# 查询当前病例的扫描数据,并将第一个扫描结果存储到scan变量中
scan = pl.query(pl.Scan).filter(pl.Scan.patient_id == example).first()
print(scan)
1.1.2图像读取-(读取CT图像的patch和分割标注)
我们以数据集中的’LIDC-IDRI-0001’病例数据为例,使用pylidc库中的按照病例文件夹名字的查询的方式,将该病例的所有的数据储存在scan中。而后提取所有专家对图像分割的标注坐标和肺结节的体素立方体。一个病例中含有多个肺结节默认提取第一个。使用的plt画图功能展示。代码如下
import numpy as np
import matplotlib.pyplot as plt
import matplotlib.animation as manim
from skimage.measure import find_contours
import cv2
import pylidc as pl
from pylidc.utils import consensus
import os
dataset_path = r'G:\dataset_zhang\LIDC-IDRI\\'
dicom_name = 'LIDC-IDRI-0001'
print(dicom_name) # 打印当前DICOM文件夹的名称
PathDicom = os.path.join(dataset_path, dicom_name) # 构建当前DICOM文件夹的完整路径
# 查询当前病例的扫描数据,并将第一个扫描结果存储到scan变量中
scan = pl.query(pl.Scan).filter(pl.Scan.patient_id == dicom_name).first()
vol = scan.to_volume()# 将该扫描数据转换成数组形式的体积(volume)
# 聚类注释(nodule annotations)以获取一组注释
nods = scan.cluster_annotations()
try:
anns = nods[0] # 尝试获取第一个注释(annotation)
Malignancy = anns[0].Malignancy # 获取注释中的恶性程度(Malignancy)信息
except IndexError:
# 如果没有注释,或者无法获取第一个注释,则继续下一个DICOM文件夹
continue
# 执行共识合并(consensus consolidation)和50%的一致性水平(agreement level)。
# 我们在切片周围添加填充以提供上下文以进行查看。
cmask, cbbox, masks = consensus(anns, clevel=0.5, pad=[(0,0), (7,7), (20,20)])
# 提取相应的切片进行可视化
image = vol[cbbox]
k = int(0.5 * (cbbox[2].stop - cbbox[2].start))
fig, ax = plt.subplots(1, 1, figsize=(5, 5))
ax.imshow(vol[cbbox][:, :, k], cmap=plt.cm.gray, alpha=1)
# 标记不同注释的边界
colors = ['r', 'g', 'b', 'y']
for j in range(len(masks)):
for c in find_contours(masks[j][:, :, k].astype(float), 0.5):
label = "Annotation %d" % (j+1)
plt.plot(c[:, 1], c[:, 0], colors[j], label=label)
# 绘制50%共识轮廓线
for c in find_contours(cmask[:, :, k].astype(float), 0.5):
plt.plot(c[:, 1], c[:, 0], '--k', label='50% Consensus')
ax.axis('off') # 关闭坐标轴
ax.legend() # 显示图例
plt.tight_layout() # 调整布局以适应图像
plt.show() # 显示图像
结果如下:
图片中,一共有4个专家对图像的分割的结果。和黑色的所有的专家对图像分割的平均的结果,一般情况下我们使用平均结果作为我们的实验参考。

1.1.3图像归一化-(读取CT图像的patch和分割标注)
图像归一化是一种将图像的像素值重新缩放到特定范围的处理方法,通常是将像素值映射到
0,1或者−1,1之间。这有助于提高模型的稳定性和收敛速度,使得不同图像具有相似的数据分布,有利于深度学习模型的训练和性能提升。代码如下
#归一化
def normalize_hu(image):
#将输入图像的像素值(-4000 ~ 4000)归一化到0~1之间
MIN_BOUND = -1000.0
MAX_BOUND = 400.0
image = (image - MIN_BOUND) / (MAX_BOUND - MIN_BOUND)
image[image > 1] = 1.
image[image < 0] = 0.
return image
1.2 图像标注信息预处理-(读取肺结节是良性还是恶性)
这段代码根据变量Malignancy的不同取值(如"Highly Unlikely"、"Moderately Unlikely"等),为label1赋予相应的标签(1到5)。通过这个过程,将文本标签映射为数字标签,方便后续机器学习模型的处理和训练。
if Malignancy == 'Highly Unlikely':
label1 = 1
elif Malignancy == 'Moderately Unlikely':
label1 = 2
elif Malignancy == 'Indeterminate':
label1 = 3
elif Malignancy == 'Moderately Suspicious':
label1 = 4
elif Malignancy == 'Highly Suspicious':
label1 = 5
print(label1)
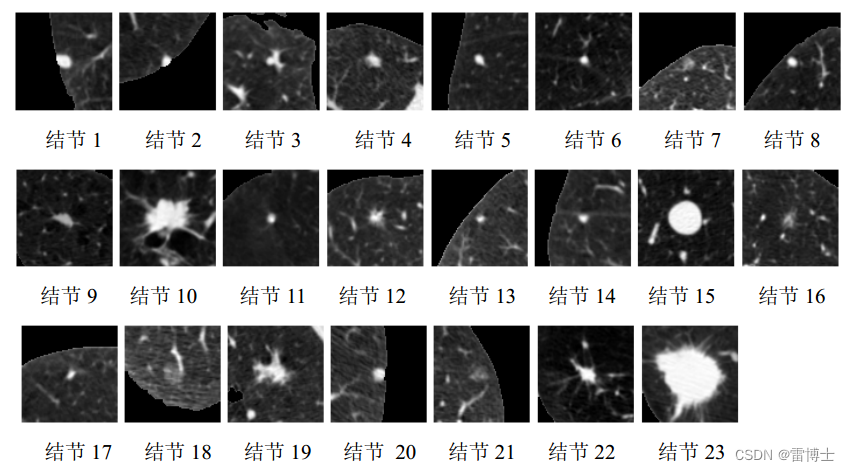
1.2 肺结节图像切片处理处理-(切片并保存)
首先根据image和cmask创建了ArrayDicom和ArrayDicom_mask矩阵。然后通过定位x_、y_、z_的中心点,对图像进行切片。接着将切片后的图像和对应的掩膜图像分别保存为大小为50x50的JPEG文件。同时,将图像的标签label1与文件名写入label.txt文件中。最后,将计数器ii增加,并输出计数器的值。
将处理后的图像进行切片和保存,并生成相应的标签信息。其中,ArrayDicom是图像数据矩阵,ArrayDicom_mask是对应的掩膜矩阵。通过对中心点定位,将图像在x、y、z方向上的切片进行大小为50x50的重采样和保存。同时,将每个图像切片的标签信息与文件名写入label.txt文件中,方便后续的数据处理和训练。
结果如下:
在label
这个label文件记录了每个图像文件的标签信息。每一行包含两个部分,以空格分隔:
第一部分是图像文件名,如 0.jpg, 1.jpg 等。
第二部分是对应图像的标签,标签是一个整数,表示图像的类别或者属性。在这个文件中,标签的含义可能是:
5: 高度可疑 (Highly Suspicious)
3: 不确定 (Indeterminate)
2: 中度可疑 (Moderately Suspicious)

1.3 总结
这样我们的就得到了我们需要训练的图像数据,它包括良性肺结节和恶性肺结节的2D图片和每一个肺结节的标签label。从三个不同方向上观察和处理图像,这在医学图像处理中是常见的。在这段代码中,每个方向的切片都被调整为大小为 (50, 50) 的图像,然后进行了插值以保持图像质量,并最终保存为 JPEG 图像文件。
“如果您有任何医学图像处理和机器学习项目需要技术支持,请随时私信我哦。”
有了这些文件我们就能够进行我们的放射组学特征的提取啦
完整代码如下:
import numpy as np
import matplotlib.pyplot as plt
import matplotlib.animation as manim
from skimage.measure import find_contours
import cv2
import pylidc as pl
from pylidc.utils import consensus
import os
dataset_path = r'G:\dataset_zhang\LIDC-IDRI\\'
dicom_name = 'LIDC-IDRI-0001'
#归一化
def normalize_hu(image):
#将输入图像的像素值(-4000 ~ 4000)归一化到0~1之间
MIN_BOUND = -1000.0
MAX_BOUND = 400.0
image = (image - MIN_BOUND) / (MAX_BOUND - MIN_BOUND)
image[image > 1] = 1.
image[image < 0] = 0.
return image
ii = 0
# Query for a scan, and convert it to an array volume.
for dicom_name in os.listdir(dataset_path):
print(dicom_name)
PathDicom = os.path.join(dicom_name)
scan = pl.query(pl.Scan).filter(pl.Scan.patient_id == dicom_name).first()
vol = scan.to_volume()
# Cluster the annotations for the scan, and grab one.
nods = scan.cluster_annotations()
try :
anns = nods[0]
Malignancy = anns[0]
Malignancy = Malignancy.Malignancy
except :
pass
# Perform a consensus consolidation and 50% agreement level.
# We pad the slices to add context for viewing.
cmask,cbbox,masks = consensus(anns, clevel=0.5,
pad=[(0,0), (7,7), (20,20)])
image = vol[cbbox]
image = normalize_hu(image)
k = int(0.5*(cbbox[2].stop - cbbox[2].start))
if Malignancy == 'Highly Unlikely':
label1 = 1
elif Malignancy == 'Moderately Unlikely':
label1 = 2
elif Malignancy == 'Indeterminate':
label1 = 3
elif Malignancy == 'Moderately Suspicious':
label1 = 4
elif Malignancy == 'Highly Suspicious':
label1 = 5
print(label1)
# 矩阵增广和传参
ArrayDicom = image
ArrayDicom_mask = cmask
# 中心点定位
x_, y_, z_ = np.shape(image)
x_ = int(x_ / 2)
y_ = int(y_ / 2)
z_ = int(z_ / 2)
# 图像进行切片处
save_dir = r'F:\test\data\train' # 修改为标签存放的位置
# 检查并创建文件夹
train_dirs = [ 'z', 'x', 'y']
for directory in train_dirs:
full_dir = os.path.join(save_dir, directory)
if not os.path.exists(full_dir):
os.makedirs(full_dir)
# label信息保存
txtfile = open(os.path.join(save_dir, 'label.txt'), mode='a')
txtfile.writelines('%s %d \n' % (str(ii)+'.jpg', label1))
txtfile.close()
# z方向切片
z_silc_50 = ArrayDicom[:, :, z_]
z_silc_50 = cv2.resize(z_silc_50, (50, 50), interpolation=cv2.INTER_LINEAR) * 255
z_silc_50 = z_silc_50.astype(np.uint8) # 数据类型转换
cv2.imwrite(os.path.join(save_dir, 'z', str(ii) + '.jpg'), z_silc_50)
# x方向切片
x_silc_50 = ArrayDicom[x_, :, :]
x_silc_50 = cv2.resize(x_silc_50, (50, 50), interpolation=cv2.INTER_LINEAR) * 255
x_silc_50 = x_silc_50.astype(np.uint8) # 数据类型转换
cv2.imwrite(os.path.join(save_dir, 'x', str(ii) + '.jpg'), x_silc_50)
# y方向切片
y_silc_50 = ArrayDicom[:, y_, :]
y_silc_50 = cv2.resize(y_silc_50, (50, 50), interpolation=cv2.INTER_LINEAR) * 255
y_silc_50 = y_silc_50.astype(np.uint8) # 数据类型转换
cv2.imwrite(os.path.join(save_dir, 'y', str(ii) + '.jpg'), y_silc_50)
ii += 1
print(ii)
请保护原创,转载不注明出处,将追究负法律责任!!!
标签:
相关文章
最新发布
- 光流法结合深度学习神经网络的原理及应用(完整代码都有Python opencv)
- Python 图像处理进阶:特征提取与图像分类
- 大数据可视化分析-基于python的电影数据分析及可视化系统_9532dr50
- 【Python】入门(运算、输出、数据类型)
- 【Python】第一弹---解锁编程新世界:深入理解计算机基础与Python入门指南
- 华为OD机试E卷 --第k个排列 --24年OD统一考试(Java & JS & Python & C & C++)
- Python已安装包在import时报错未找到的解决方法
- 【Python】自动化神器PyAutoGUI —告别手动操作,一键模拟鼠标键盘,玩转微信及各种软件自动化
- Pycharm连接SQL Sever(详细教程)
- Python编程练习题及解析(49题)
点击排行
- 版本匹配指南:Numpy版本和Python版本的对应关系
- 版本匹配指南:PyTorch版本、torchvision 版本和Python版本的对应关系
- Python 可视化 web 神器:streamlit、Gradio、dash、nicegui;低代码 Python Web 框架:PyWebIO
- 相关性分析——Pearson相关系数+热力图(附data和Python完整代码)
- Anaconda版本和Python版本对应关系(持续更新...)
- Python与PyTorch的版本对应
- Windows上安装 Python 环境并配置环境变量 (超详细教程)
- Python pyinstaller打包exe最完整教程

